【JSTnews3月号掲載】NEWS&TOPICS 戦略的創造研究推進事業さきがけ/研究領域「時空間マルチスケール計測に基づく生物の復元あるいは多様化を実現する機構の解明」 研究課題「『不都合な配列』解析で切り拓く翻訳制御と生命力の理解」
バイオものづくりにつながる、合成困難なアミノ酸配列パターンを細菌に発見
2026年03月16日 12時00分更新
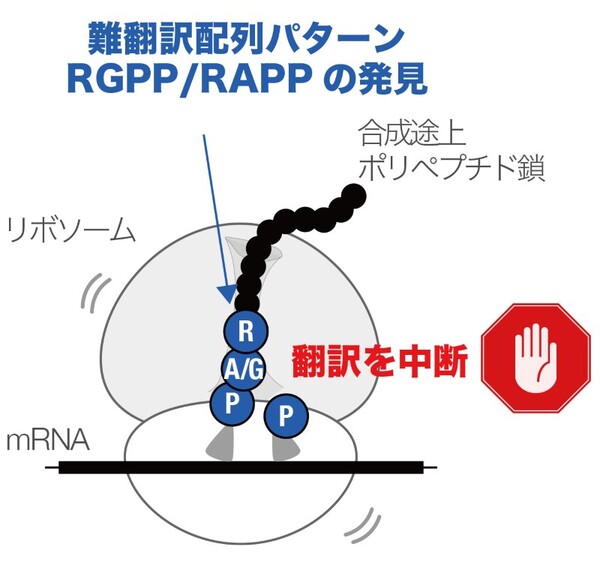
細胞内では、リボソームが遺伝情報を担うDNAに従って20種類のアミノ酸を特定の並び順で数十~数千個連結してたんぱく質を合成します。最近になり、リボソームにとって合成が困難なアミノ酸配列があることがわかってきました。こうしたアミノ酸配列を「難翻訳配列」と呼びます。たんぱく質の合成を止めてしまう難翻訳配列は本来、生物にとって不都合なものであり、その存在が生物の進化にどのような影響を与えてきたのか知ることは極めて重要です。
国立遺伝学研究所の藤原圭吾特命助教と京都産業大学の千葉志信教授らの研究グループは、細菌が共通に持つ難翻訳配列のパターンを見つけ、さらに難翻訳配列を積極的に利用して働く特異なたんぱく質群があることを明らかにしました。同グループはまず、系統的な変異解析により、アルギニンーグリシンープロリンープロリン(RGPP)や、アルギニンーアラニンープロリンープロリン(RAPP)というアミノ酸配列が含まれると難翻訳配列になりやすいことを突き止めました。次に、細菌界全体を網羅した遺伝情報の解析から、RGPP配列が細菌界で最も出現頻度が低いことを発見。さらに、RAPPやRGPPという配列をカルボキシ末端付近に持つたんぱく質が多い放線菌に着目し、生物情報学的な解析によってこれらのたんぱく質が、細胞内外の環境を監視して適応するために働くと思われる未知の生理機能を持つことを示しました。
今回の成果は、遺伝情報の進化や遺伝子発現、翻訳の分子機構を理解する基礎的な知見となります。細菌や微生物を利用して有用化合物を生産する「バイオものづくり」や抗生物質の開発でも有用となると考えられます。

この連載の記事
-
第79回
TECH
水電解における塩素発生の抑制につながる新発見 -
第78回
TECH
情報通信科学分野の革新的技術の創出を見据え、JSTと情報通信研究機構(NICT)が業務連携 -
第77回
TECH
農業用ハウスの屋根に載せられる有機太陽電池~農作物育成と発電が両立可能に -
第76回
TECH
昆虫の「求愛歌」の仕組みを解明し、ハエや蚊の繁殖を抑える技術へ -
第75回
TECH
情報学・神経生理学・社会心理学の学際的研究で、AI によるおすすめの信頼性を向上! -
第74回
TECH
白亜紀から続くロマンに惹かれて挑む、浮遊性有孔虫の研究 -
第73回
TECH
出芽酵母を用いて環状DNA発生の仕組みを明らかに -
第72回
TECH
病原細菌が植物の葉の気孔を開いて侵入する仕組みを発見 -
第71回
TECH
原子分解能電子顕微鏡法で、結晶粒境界における添加元素の拡散状況を観察 -
第70回
TECH
有機フッ素化合物を分解する新たな技術を開発 - この連載の一覧へ